相关产品推荐更多 >
万千商家帮你免费找货
0 人在求购买到急需产品
- 详细信息
- 询价记录
- 文献和实验
- 技术资料
- 库存:
有
- 供应商:
环亚生物科技有限公司
- 现货状态:
有
- 保修期:
1年
Pippin ELF 全自动DNA分选纯化仪
—可将DNA样品按大小回收成12个组份,还可以用于回收蛋白
• Sage Science 公司
位于美国马萨诸塞州,2010年成立,专注于核酸领域的样品制备
全球超过3000家客户的认可,国内装机数量400台左右
2万篇文献中应用,包括众多Nature、 Science、 Cell系列的文章
DNA片段筛选回收领域的行业金标准
• Pippin ELF 全自动DNA分选纯化仪
自动化完成核酸片段大小范围的回收(size-selection)
用于从单一样本构建多个不同长度的文库,或者是RNA iso-form / splice variant detection转录异构体的建库、或是珍贵样本的建库等
自带脉冲场模块,实现100bp-40kb范围内的DNA样本分离回收效果;也可以实现蛋白回收
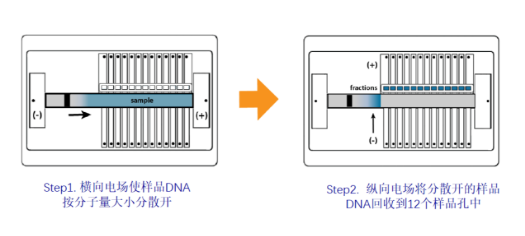
技术原理
- 上样后,首先通过横向电泳将DNA按分子量大小分散开
- 横向电场关闭,纵向电场打开,将样品回收至12个样品孔中
- 自带脉冲场电泳程序,对于10kb以上的大片段DNA也有优异的分离效果
产品特点
- 将DNA样本通过电泳分离后回收至12个样品孔中
- 每个组分可以单独建库或用于下一步实验
- 实现对DNA样本更高效、精准的回收
应用方向

典型案例
|
加利福尼亚大学、耶鲁大学、哈佛大学等多个科研单位,联合开展研究绘制出了人类泛基因组参考图谱。相关成果在国际权威期刊《Nature》杂志发表。 文章中Sage ELF用于HiFi文库片段筛选(Liao, Wen-Wei, et al. "A draft human pangenome reference." Nature 617.7960 (2023): 312-324.)
|
代表客户

风险提示:丁香通仅作为第三方平台,为商家信息发布提供平台空间。用户咨询产品时请注意保护个人信息及财产安全,合理判断,谨慎选购商品,商家和用户对交易行为负责。对于医疗器械类产品,请先查证核实企业经营资质和医疗器械产品注册证情况。
- 作者
- 内容
- 询问日期
 文献和实验
文献和实验发表文献
|
1.Kratochwil, Claudius F., et al. "An intronic transposon insertion associates with a trans-species color polymorphism in Midas cichlid fishes." Nature Communications 13.1 (2022): 296. 2.Bickhart, Derek M., et al. "Generating lineage-resolved, complete metagenome-assembled genomes from complex microbial communities." Nature biotechnology 40.5 (2022): 711-719. 3.Kuhl, Heiner, et al. "Equilibrated evolution of the mixed auto-/allopolyploid haplotype-resolved genome of the invasive hexaploid Prussian carp." Nature communications 13.1 (2022): 4092. 4.Jarvis, Erich D., et al. "Semi-automated assembly of high-quality diploid human reference genomes." Nature (2022): 1-13. 5.Cerca, José, et al. "The genomic basis of the plant island syndrome in Darwin’s giant daisies." Nature communications 13.1 (2022): 3729. 6.Zou, Changsong, et al. "The genome of broomcorn millet." Nature communications 10.1 (2019): 436. 7.Kolmogorov, Mikhail, et al. "metaFlye: scalable long-read metagenome assembly using repeat graphs." Nature Methods 17.11 (2020): 1103-1110. 8.Wenger, Aaron M., et al. "Accurate circular consensus long-read sequencing improves variant detection and assembly of a human genome." Nature biotechnology 37.10 (2019): 1155-1162. 9.Wu, Zhikun, et al. "Structural variants in the Chinese population and their impact on phenotypes, diseases and population adaptation." Nature Communications 12.1 (2021): 6501. 10.Sun, Yu H., et al. "Single-molecule long-read sequencing reveals a conserved intact long RNA profile in sperm." Nature communications 12.1 (2021): 1361. |
 技术资料
技术资料暂无技术资料 索取技术资料











