相关产品推荐更多 >
万千商家帮你免费找货
0 人在求购买到急需产品
- 详细信息
- 文献和实验
- 技术资料
- 品系:
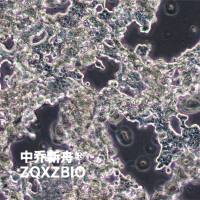
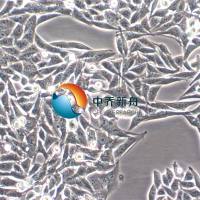
细胞系
- 供应商:
中乔新舟
- 库存:
1000
- 英文名:
REC1
- 生长状态:
悬浮
- 年限:
液氮长期
- 运输方式:
常温运输
- 物种来源:
人
- 规格:
T25
|
产品名称 |
REC1人套细胞淋巴瘤细胞 |
|
货号 |
ZQ1092 |
|
产品介绍 |
REC-1是一种人套细胞淋巴瘤细胞系,源自2003年一位57岁男性的淋巴结中分离出的淋巴母细胞系,该患者患有终末难治性B细胞非霍奇金淋巴瘤。REC-1细胞系是由携带T(11;14)(Q13;Q32)的淋巴瘤建立的,这一染色体易位是套细胞淋巴瘤的特征之一,可用于免疫学研究。 |
|
种属 |
人 |
|
性别/年龄 |
男/57岁 |
|
组织 |
淋巴结 |
|
疾病 |
套细胞淋巴瘤 |
|
细胞类型 |
肿瘤细胞 |
|
形态学 |
淋巴母细胞 |
|
生长方式 |
悬浮 |
|
倍增时间 |
大约:38 hours (PubMed=25315077); ~38 hours (ATCC=CRL-3004); ~20-40 hours (DSMZ=ACC-584) |
|
培养基和添加剂 |
RPMI-1640(品牌:中乔新舟 货号:ZQ-200)+10%胎牛血清(中乔新舟 货号:ZQ500-A)+1%P/S(中乔新舟 货号:CSP006) |
|
推荐完全培养基货号 |
ZM1092 |
|
生物安全等级 |
BSL-1 |
|
培养条件 |
95%空气,5%二氧化碳;37℃ |
|
STR位点信息 |
Amelogenin: X,Y CSF1PO :10,12 D2S1338: 17 D3S1358 :15,16 D5S818: 12,13 D7S820: 10,11 D8S1179 :11,12 D13S317: 10 D16S539: 11 D18S51: 14,16 D19S433: 14,15 D21S11 :28,29 FGA :22,23 Penta D: 9,13 Penta E: 7 (PubMed=25877200) :7,19 (DSMZ=ACC-584) :19 (ATCC=CRL-3004) TH01: 9,9.3 TPOX: 8,9 vWA :17 |
|
抗原表达/受体表达 |
*** |
|
基因表达 |
*** |
|
保藏机构 |
ATCC; CRL-3004 ,DSMZ; ACC-584 ,IZSLER; BS TCL 227 |
|
供应限制 |
仅供科研使用 |
上海中乔新舟生物科技有限公司成立于2011年,历经十多年发展,主要专注于细胞生物学产品的研究和开发,专注于为药企、各类科研机构及CRO企业提供符合标准规范的细胞培养服务、细胞培养基、细胞检测试剂盒、细胞培养试剂,胎牛血清和细胞生物学技术服务等。
公司一直致力于为高等院校、研究机构、医院、CRO及CDMO企业提供细胞培养完整解决方案,这些产品旨在满足细胞培养的多样需求,确保实验和研究的有效进行。引用中乔新舟(ZQXZBIO)产品和服务的文献超数千篇。

产品服务
细胞资源:原代细胞、细胞株、干细胞、示踪细胞、耐药株细胞、永生化细胞等基因工程细胞。
试剂产品:胎牛血清、完全培养基(适用于原代细胞及细胞株)、无血清培养基、基础培养基、细胞转染试剂、重组因子、胰酶和双抗等等细胞培养所有实验相关产品。
技术服务:稳转株构建、原代细胞分离、特殊培养基定制服务、细胞检测等。

目前产品已经畅销国内30多个省市,与客户建立长期的合作伙伴关系,共同实现成功。全体员工将不懈努力,继续为科研人员提供优良的产品和服务,致力成为全球细胞培养领域的参与者。
企业愿景
致力于成为国内细胞培养基产业的佼佼者,生物医药领域上游原材料的优良提供商。
企业使命
成长为专业细胞系及原代细胞培养供应商、专业细胞培养基及培养试剂生产商。
企业荣誉


风险提示:丁香通仅作为第三方平台,为商家信息发布提供平台空间。用户咨询产品时请注意保护个人信息及财产安全,合理判断,谨慎选购商品,商家和用户对交易行为负责。对于医疗器械类产品,请先查证核实企业经营资质和医疗器械产品注册证情况。
 文献和实验
文献和实验
PubMed=1572647; DOI=10.1016/0888-7543(92)90303-A
Szepetowski P., Simon M.-P., Grosgeorge J., Huebner K., Bastard C., Evans G.A., Tsujimoto Y., Birnbaum D., Theillet C., Gaudray P.
Localization of 11q13 loci with respect to regional chromosomal breakpoints.
Genomics 12:738-744(1992)
PubMed=7504521; DOI=10.1002/gcc.2870080204
Raynaud S.D., Bekri S., Leroux D., Grosgeorge J., Klein B., Bastard C., Gaudray P., Simon M.-P.
Expanded range of 11q13 breakpoints with differing patterns of cyclin D1 expression in B-cell malignancies.
Genes Chromosomes Cancer 8:80-87(1993)
PubMed=8558920
Dirks W.G., Zaborski M., Jager K., Challier C., Shiota M., Quentmeier H., Drexler H.G.
The (2;5)(p23;q35) translocation in cell lines derived from malignant lymphomas: absence of t(2;5) in Hodgkin-analogous cell lines.
Leukemia 10:142-149(1996)
PubMed=14973505; DOI=10.1038/sj.leu.2403315
Prod'homme T., Drenou B., De Ruyffelaere C., Barbieri G., Wiszniewski W., Bastard C., Charron D., Alcaide-Loridan C.
Defective class II transactivator expression in a B lymphoma cell line.
Leukemia 18:832-840(2004)
PubMed=15126345; DOI=10.1158/0008-5472.CAN-03-3773
Ota A., Tagawa H., Karnan S., Tsuzuki S., Karpas A., Kira S., Yoshida Y., Seto M.
Identification and characterization of a novel gene, C13orf25, as a target for 13q31-q32 amplification in malignant lymphoma.
Cancer Res. 64:3087-3095(2004)
PubMed=16448697; DOI=10.1016/j.leukres.2005.11.013
Camps J., Salaverria I., Garcia M.J., Prat E., Bea S., Pole J.C.M., Hernandez L., Del Rey J., Cigudosa J.C., Bernues M., Caldas C., Colomer D., Miro R., Campo E.
Genomic imbalances and patterns of karyotypic variability in mantle-cell lymphoma cell lines.
Leuk. Res. 30:923-934(2006)
PubMed=16960149; DOI=10.1182/blood-2006-06-026500
Mestre-Escorihuela C., Rubio-Moscardo F., Richter J.A., Siebert R., Climent J., Fresquet V., Beltran E., Agirre X., Marugan I., Marin M., Rosenwald A., Sugimoto K.-j., Wheat L.M., Karran E.L., Garcia J.F., Sanchez-Verde L., Prosper F., Staudt L.M., Pinkel D., Dyer M.J.S., Martinez-Climent J.A.
Homozygous deletions localize novel tumor suppressor genes in B-cell lymphomas.
Blood 109:271-280(2007)
PubMed=17332242; DOI=10.1182/blood-2006-11-057208
Pinyol M., Bea S., Pla L., Ribrag V., Bosq J., Rosenwald A., Campo E., Jares P.
Inactivation of RB1 in mantle-cell lymphoma detected by nonsense-mediated mRNA decay pathway inhibition and microarray analysis.
Blood 109:5422-5429(2007)
PubMed=20215515; DOI=10.1158/0008-5472.CAN-09-3458
Rothenberg S.M., Mohapatra G., Rivera M.N., Winokur D., Greninger P., Nitta M., Sadow P.M., Sooriyakumar G., Brannigan B.W., Ulman M.J., Perera R.M., Wang R., Tam A., Ma X.-J., Erlander M., Sgroi D.C., Rocco J.W., Lingen M.W., Cohen E.E.W., Louis D.N., Settleman J., Haber D.A.
A genome-wide screen for microdeletions reveals disruption of polarity complex genes in diverse human cancers.
Cancer Res. 70:2158-2164(2010)
PubMed=21746927; DOI=10.1073/pnas.1018941108
Beltran E., Fresquet V., Martinez-Useros J., Richter-Larrea J.A., Sagardoy A., Sesma I., Almada L.L., Montes-Moreno S., Siebert R., Gesk S., Calasanz M.J., Malumbres R., Rieger M., Prosper F., Lossos I.S., Piris M.A., Fernandez-Zapico M.E., Martinez-Climent J.A.
A cyclin-D1 interaction with BAX underlies its oncogenic role and potential as a therapeutic target in mantle cell lymphoma.
Proc. Natl. Acad. Sci. U.S.A. 108:12461-12466(2011)
PubMed=22460905; DOI=10.1038/nature11003
Barretina J.G., Caponigro G., Stransky N., Venkatesan K., Margolin A.A., Kim S., Wilson C.J., Lehar J., Kryukov G.V., Sonkin D., Reddy A., Liu M., Murray L., Berger M.F., Monahan J.E., Morais P., Meltzer J., Korejwa A., Jane-Valbuena J., Mapa F.A., Thibault J., Bric-Furlong E., Raman P., Shipway A., Engels I.H., Cheng J., Yu G.-Y.K., Yu J.-J., Aspesi P. Jr., de Silva M., Jagtap K., Jones M.D., Wang L., Hatton C., Palescandolo E., Gupta S., Mahan S., Sougnez C., Onofrio R.C., Liefeld T., MacConaill L.E., Winckler W., Reich M., Li N.-X., Mesirov J.P., Gabriel S.B., Getz G., Ardlie K., Chan V., Myer V.E., Weber B.L., Porter J., Warmuth M., Finan P., Harris J.L., Meyerson M.L., Golub T.R., Morrissey M.P., Sellers W.R., Schlegel R., Garraway L.A.
The Cancer Cell Line Encyclopedia enables predictive modelling of anticancer drug sensitivity.
Nature 483:603-607(2012)
PubMed=24362935; DOI=10.1038/nm.3435
Rahal R., Frick M., Romero R., Korn J.M., Kridel R., Chan F.C., Meissner B., Bhang H.-E.C., Ruddy D., Kauffmann A., Farsidjani A., Derti A., Rakiec D., Naylor T., Pfister E., Kovats S., Kim S., Dietze K., Dorken B., Steidl C., Tzankov A., Hummel M., Monahan J., Morrissey M.P., Fritsch C., Sellers W.R., Cooke V.G., Gascoyne R.D., Lenz G., Stegmeier F.
Pharmacological and genomic profiling identifies NF-kappaB-targeted treatment strategies for mantle cell lymphoma.
Nat. Med. 20:87-92(2014)
PubMed=25960936; DOI=10.4161/21624011.2014.954893
Boegel S., Lower M., Bukur T., Sahin U., Castle J.C.
A catalog of HLA type, HLA expression, and neo-epitope candidates in human cancer cell lines.
OncoImmunology 3:e954893.1-e954893.12(2014)
PubMed=25315077; DOI=10.3109/10428194.2014.970548
Fogli L.K., Williams M.E., Connors J.M., Reid Y.A., Brown K., O'Connor O.A.
Development and characterization of a Mantle Cell Lymphoma Cell Bank in the American Type Culture Collection.
Leuk. Lymphoma 56:2114-2122(2015)
PubMed=25355872; DOI=10.1128/JVI.02570-14
Cao S.-B., Strong M.J., Wang X., Moss W.N., Concha M., Lin Z., O'Grady T., Baddoo M., Fewell C., Renne R., Flemington E.K.
High-throughput RNA sequencing-based virome analysis of 50 lymphoma cell lines from the Cancer Cell Line Encyclopedia project.
J. Virol. 89:713-729(2015)
PubMed=25485619; DOI=10.1038/nbt.3080
Klijn C., Durinck S., Stawiski E.W., Haverty P.M., Jiang Z.-S., Liu H.-B., Degenhardt J., Mayba O., Gnad F., Liu J.-F., Pau G., Reeder J., Cao Y., Mukhyala K., Selvaraj S.K., Yu M.-M., Zynda G.J., Brauer M.J., Wu T.D., Gentleman R.C., Manning G., Yauch R.L., Bourgon R., Stokoe D., Modrusan Z., Neve R.M., de Sauvage F.J., Settleman J., Seshagiri S., Zhang Z.-M.
A comprehensive transcriptional portrait of human cancer cell lines.
Nat. Biotechnol. 33:306-312(2015)
PubMed=25688540; DOI=10.1002/cyto.a.22643
Maiga S., Brosseau C., Descamps G., Dousset C., Gomez-Bougie P., Chiron D., Menoret E., Kervoelen C., Vie H., Cesbron A., Moreau-Aubry A., Amiot M., Pellat-Deceunynck C.
A simple flow cytometry-based barcode for routine authentication of multiple myeloma and mantle cell lymphoma cell lines.
Cytometry A 87:285-288(2015)
PubMed=25877200; DOI=10.1038/nature14397
Yu M., Selvaraj S.K., Liang-Chu M.M.Y., Aghajani S., Busse M., Yuan J., Lee G., Peale F.V., Klijn C., Bourgon R., Kaminker J.S., Neve R.M.
A resource for cell line authentication, annotation and quality control.
Nature 520:307-311(2015)
PubMed=26589293; DOI=10.1186/s13073-015-0240-5
Scholtalbers J., Boegel S., Bukur T., Byl M., Goerges S., Sorn P., Loewer M., Sahin U., Castle J.C.
TCLP: an online cancer cell line catalogue integrating HLA type, predicted neo-epitopes, virus and gene expression.
Genome Med. 7:118.1-118.7(2015)
PubMed=28196595; DOI=10.1016/j.ccell.2017.01.005
Li J., Zhao W., Akbani R., Liu W.-B., Ju Z.-L., Ling S.-Y., Vellano C.P., Roebuck P., Yu Q.-H., Eterovic A.K., Byers L.A., Davies M.A., Deng W.-L., Gopal Y.N.V., Chen G., von Euw E.M., Slamon D.J., Conklin D., Heymach J.V., Gazdar A.F., Minna J.D., Myers J.N., Lu Y.-L., Mills G.B., Liang H.
Characterization of human cancer cell lines by reverse-phase protein arrays.
Cancer Cell 31:225-239(2017)
PubMed=29666304; DOI=10.1158/1078-0432.CCR-17-3004
Pham L.V., Huang S.-J., Zhang H., Zhang J., Bell T., Zhou S.-H., Pogue E., Ding Z.-Y., Lam L., Westin J., Davis R.E., Young K.H., Medeiros L.J., Ford R.J. Jr., Nomie K., Zhang L., Wang M.
Strategic therapeutic targeting to overcome venetoclax resistance in aggressive B-cell lymphomas.
Clin. Cancer Res. 24:3967-3980(2018)
PubMed=30285677; DOI=10.1186/s12885-018-4840-5
Tan K.-T., Ding L.-W., Sun Q.-Y., Lao Z.-T., Chien W., Ren X., Xiao J.-F., Loh X.-Y., Xu L., Lill M., Mayakonda A., Lin D.-C., Yang H., Koeffler H.P.
Profiling the B/T cell receptor repertoire of lymphocyte derived cell lines.
BMC Cancer 18:940.1-940.13(2018)
PubMed=30629668; DOI=10.1371/journal.pone.0210404
Uphoff C.C., Pommerenke C., Denkmann S.A., Drexler H.G.
Screening human cell lines for viral infections applying RNA-Seq data analysis.
PLoS ONE 14:E0210404-E0210404(2019)
PubMed=30894373; DOI=10.1158/0008-5472.CAN-18-2747
Dutil J., Chen Z.-H., Monteiro A.N.A., Teer J.K., Eschrich S.A.
An interactive resource to probe genetic diversity and estimated ancestry in cancer cell lines.
Cancer Res. 79:1263-1273(2019)
PubMed=31068700; DOI=10.1038/s41586-019-1186-3
Ghandi M., Huang F.W., Jane-Valbuena J., Kryukov G.V., Lo C.C., McDonald E.R. III, Barretina J.G., Gelfand E.T., Bielski C.M., Li H.-X., Hu K., Andreev-Drakhlin A.Y., Kim J., Hess J.M., Haas B.J., Aguet F., Weir B.A., Rothberg M.V., Paolella B.R., Lawrence M.S., Akbani R., Lu Y.-L., Tiv H.L., Gokhale P.C., de Weck A., Mansour A.A., Oh C., Shih J., Hadi K., Rosen Y., Bistline J., Venkatesan K., Reddy A., Sonkin D., Liu M., Lehar J., Korn J.M., Porter D.A., Jones M.D., Golji J., Caponigro G., Taylor J.E., Dunning C.M., Creech A.L., Warren A.C., McFarland J.M., Zamanighomi M., Kauffmann A., Stransky N., Imielinski M., Maruvka Y.E., Cherniack A.D., Tsherniak A., Vazquez F., Jaffe J.D., Lane A.A., Weinstock D.M., Johannessen C.M., Morrissey M.P., Stegmeier F., Schlegel R., Hahn W.C., Getz G., Mills G.B., Boehm J.S., Golub T.R., Garraway L.A., Sellers W.R.
Next-generation characterization of the Cancer Cell Line Encyclopedia.
Nature 569:503-508(2019)
PubMed=31160637; DOI=10.1038/s41598-019-44491-x
Quentmeier H., Pommerenke C., Dirks W.G., Eberth S., Koeppel M., MacLeod R.A.F., Nagel S., Steube K., Uphoff C.C., Drexler H.G.
The LL-100 panel: 100 cell lines for blood cancer studies.
Sci. Rep. 9:8218-8218(2019)
PubMed=31978347; DOI=10.1016/j.cell.2019.12.023
Nusinow D.P., Szpyt J., Ghandi M., Rose C.M., McDonald E.R. III, Kalocsay M., Jane-Valbuena J., Gelfand E.T., Schweppe D.K., Jedrychowski M.P., Golji J., Porter D.A., Rejtar T., Wang Y.K., Kryukov G.V., Stegmeier F., Erickson B.K., Garraway L.A., Sellers W.R., Gygi S.P.
Quantitative proteomics of the Cancer Cell Line Encyclopedia.
Cell 180:387-402.e16(2020)
癌和套细胞淋巴瘤中低表达的miR-15a-miR-16-1簇,靶向致癌基因cyclin D1。6. 值得注意的是,这些miRNA的作用是组织和肿瘤特异性的,例如miR-155在白血病和淋巴癌中是高度表达的,并起着原癌基因的作用,而miR-155在内分泌肿瘤中表达极大地下调,很可能对内分泌肿瘤具有抑制作用。7. 最新的研究发现,许多miRNA参与晚期癌症的特征--癌细胞扩散过程的调控,这些miRNA通过同时作用多条信号通路并靶向不同目标蛋白基因而对癌细胞扩散起激活或抑制的功能。 8. 肿瘤转移中
位点常有缺失,而这一位点并不存在已知的抑癌基因。 65%B细胞慢性淋巴型白血病(CLL)病人,50%的套细胞淋巴瘤病人,16-40%的骨髓瘤病人、60%的前列腺癌病人中有13q14位点的缺失。因此,在这个30Kb的区域中必定有一个肿瘤抑制基因的存在。而mir-15a和mir-16-1位于这一区域中一个功能未知的被称为LEU2的非编码蛋白的RNA基因的内含子区域。Climmino等最近报道,miR-15a和miR-16-1负调控BCL2,一个抗凋亡基因,因此,这两个miRNAs的缺失
9.29 曹雪涛院士 Science 揭示 m6A 介导的细胞代谢重编程抑制病毒感染机制
receptor, BAFF-R)的 CAR-T 细胞根除了动物模型中对 CD19 靶向疗法产生抵抗性的人白血病细胞和淋巴瘤细胞。在这项新的研究中,携带 CD19 治疗抗性的人类肿瘤(包括伯基特淋巴瘤、套细胞淋巴瘤和其他的非霍奇金淋巴瘤亚型,以及急性淋巴细胞白血病)的动物模型接受了 BAFF-R CAR-T 细胞治疗。在接受这些 CAR-T 细胞治疗后,他们观察到明显的肿瘤消退和延长的生存期。在携带人类伯基特淋巴瘤的动物模型中,它们在接受单次 BAFF-R CAR-T 治疗后即可治愈(肿瘤完全消退,长期
 技术资料
技术资料暂无技术资料 索取技术资料