大家都在搜
| 喜报: 近日,华银健康下属子公司广州华银医学检验中心自主研发的《基于分子标记的免疫组库生物信息分析方法》发明专利获得授权。一直以来,华银健康高通量测序事业部都专注于免疫组库测序技术难题的攻克,该专利技术获得授权,标志着华银健康在免疫组库高通量测序产品研发上的重大突破,也标志着华银健康自主创新水平再上新台阶。  人类或哺乳动物的适应性免疫系统拥有大量的 T 细胞受体 (TCRs)和 B 细胞受体(BCRs),其总和统称为免疫组库。免疫组库高通量测序技术允许对 T 或 B 细胞克隆进行深入分析,可以有效评估 TCR/BCR 互补决定区域(CDR3)的多样性,并评估克隆类型的构成:包括特定克隆类型的比例; 克隆之间的相似程度;V(D)J 的基因使用频率; 核苷酸插入与缺失;CDR3 区域长度分布等信息,为评估健康或疾病状态下的机体适应性免疫系统提供了可能。 华银健康作为国内最早开展免疫组库项目研发的团队之一,早于 2016 年便与南方医科大学(前第一军医大学)的科研团队深度合作,并成功发表学术论文(Chen, et al. OncoImmunology (2016))。 此次华银健康推出的全新免疫组库测序产品,其基于 5'RACE 的原理,在原始模板扩增前引入 UMI 序列进行文库构建,并使用具有华银健康自主发明专利的 UMI 标记与校正算法(发明专利号:201810618023.7),对 PCR 扩增与测序过程引入的错误与偏倚进行有效纠正,极大提高分析结果的准确度。 专利看点一:UMI 减少错误与偏移 华银健康使用具有自主发明专利的 UMI 标记与校正算法技术,达到了 75% 以上的校正比(表 1),有效减少了测序和 PCR 扩增实验过程中所引入的错误和偏移。  图 1. UMI 标记消除测序和 PCR 扩增的错误 本项目所用的 UMI(Unique Molecular Indices,分子条形码)为 16nt 的随机碱基短序列,可以看作分子条形码。将随机 UMI 序列于逆转录阶段引入模板,标记原始样本中的每个分子,对同一来源的扩增产物进行标记;通过 UMI 标记与校正算法,可以排除 PCR 扩增偏好性和建库过程中造成的误差,并获取原始的转录本数量,达到绝对定量。  表 1. 经过 UMI 算法校正后的部分测试数据校正比例统计表 专利看点二:重复性好,稳定性高 华银健康使用具有自主发明专利的 UMI 标记与校正算法技术,发现在相同的 RNA 起始量下同一样本其相关性高且重现性好(图 2)。  图 2. 同一样本 RNA 起始量相同时样本间的相关性图(起始 RNA 量:A1/A2/A3 为 1600ng; B1/B2/B3 为 400ng) 专利看点三:微量起始,数据量快速饱和 对于 RNA 起始量低或高的样本,随着测序深度的增加,均能够快速达到测序平台期,即数据量能够满足后续分析需求 (图 3)。  图 3. 同一样本 RNA 起始量不同时到达测序饱和期数据统计曲线图 华银健康免疫组库项目分析流程能够对测序数据进行多维度深入挖掘(图 4),给出最全面的数据分析报告,并可按照客户的需求定制个性化分析服务。  图 4:数据分析条目概览 华银健康免疫组库项目部分分析结果展示: 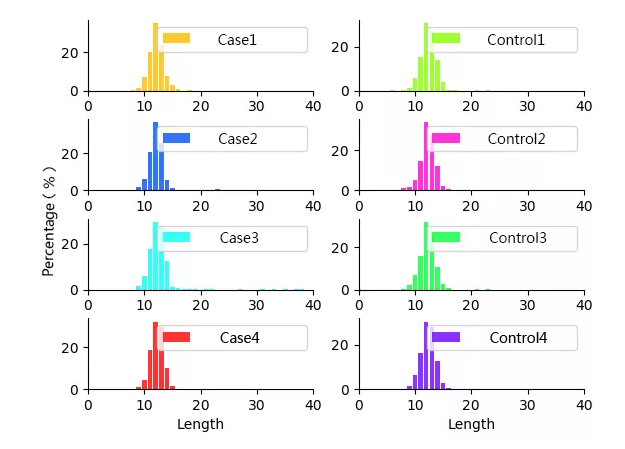 样本的 CDR3 氨基酸长度分布图  VJ Combination 统计图  样本间 VDJ 基因共线性  样本 Rank abundance 分布曲线图  样本 Diversity 分布曲线图 参考文献: 1.Abbas A K, et al. Cellular & Molecular Immunology 6e[J]. 2.Hou X L, et al. Current status and recent advances of next generation sequencing techniques in immunological repertoire[J]. Genes & Immunity, 2016, 17(3):153. 3.Lefranc, et al. "IMGT®, the international ImMunoGeneTics information system®." Nucleic acids research 37.suppl_1 (2008): D1006-D1012. 4.Chunlin Wanga,et al. High throughput sequencing reveals a complex pattern of dynamic interrelationships among human T cell subsets. PNAS, 2010, vol. 107:1518–1523. 5.Jennifer Benichou,et al. 2Rep-Seq uncovering the immunological repertoire through next-generation sequencing. Immunology, 2011, 135: 183–191. 6.Jeroen W J van Heijst,et al. Quantitative assessment of T cell repertoire recovery after hematopoietic stem cell transplantation. Nature Medicine, 2013,VOL.19: 372-379. 7.Miran Jang,et al. Characterization of T cell repertoire of blood,tumor, and ascites in ovarian cancer patients using next generation sequencing. OncoImmunology, 2015, Vol.4:e1030561-1-10. 8.Evaggelia Liaskou,et al. High-throughput T-cell receptor sequencing across chronic liver diseases reveals distinct disease-associated repertoires. Hepatology, 2015,1-10. 9.Bates S T,et al. Global biogeography of highly diverse protistan communities in soil[J]. The ISME journal, 2013,7(3): 652-659. 作者:Jayden 审核:Camile |